当我想好这个题目的时候,我顺便放狗搜了一下,找到几个非常对我胃口的博客(数据科学与R语言,Yihui Xie)。在看其中文档的过程中,我曾有短暂的失落感,“我在统计方面的知识太逊了”,不过我马上意识到自己又陷入了完美主义的坑,一个人怎能那方面都那么出色呢?在统计领域,我只要知道有哪些流行技术,哪些对我现在的研究课题有帮助,或者将来有帮助即可,只要分类整理入自己的笔记即可,完全可以等到需要的时候再去学。我自己喜欢的专业才是最根本的,这个是核心,其他只是点缀而已。我的目标是,“比药学家懂统计,比统计学家懂药学”!
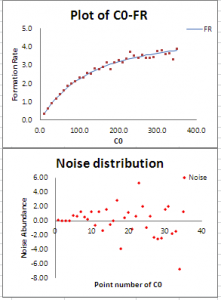
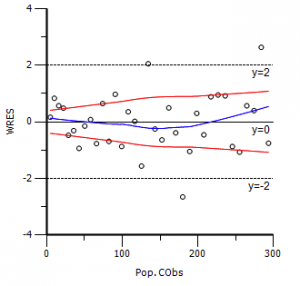
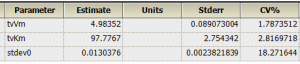
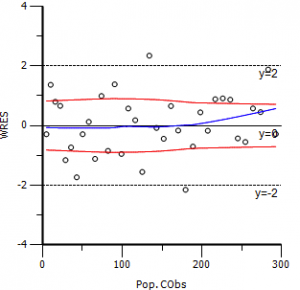
为什么会想写这个题目呢?因为今天做酶动力学的模拟实验的时候,确实发现了这种现象,只有观测变量(因变量)的误差的方差恒定时,用非线性拟合得到的参数才是无偏的。对于线性拟合,只有满足高斯–马尔科夫定理条件时(零均值、等方差、不相关),最小二乘估计才是无偏估计。应该这对非线性拟合,同样适用吧。如果观测变量的误差不满足高-马条件时(比如方差随观测变量的增大而增大,可以从残差图上看到),该如何进行无偏估计呢?其实前几天已经提到了,正是Phoenix中的可进行群体药动学分析的PML!其所采用的技术为非线性混合效应模型法,广泛用于群体药动学参数的估计,模型中包含固定效应(相当于传统的非线性模型部分)、随机效应(个体间的变异)和误差模型(这里可以针对不同类型的误差进行建模,关键所在)。下面给出一个模拟实例,来说明用NLME进行非等方差时的参数估计。
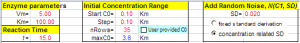
模拟数据用EnzySolver的模拟功能来实现,具体参数如下: